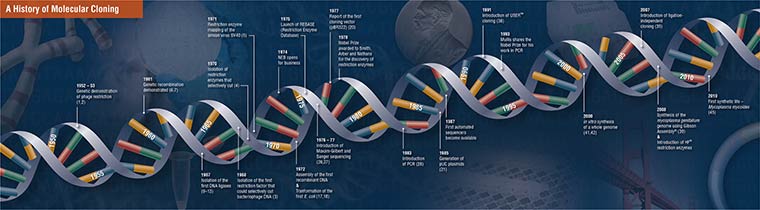
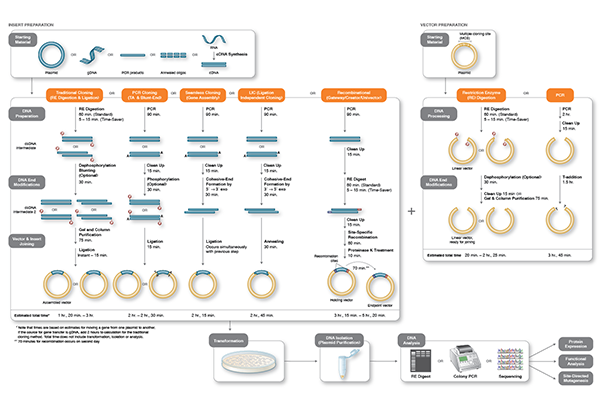
Clonage moléculaire
Le clonage moléculaire consiste à produire des molécules d’ADN recombinant et à les utiliser pour transformer un organisme hôte, dans lequel elles sont répliquées.
Principe
Une réaction de clonage moléculaire fait généralement intervenir les deux éléments suivants :
- Le fragment d’ADN d’intérêt à répliquer ;
- Un vecteur plasmidique contenant tous les composants nécessaires à sa réplication dans l’organisme hôte.
L’ADN d’intérêt (un gène, des éléments régulateurs ou un opéron, par exemple) est préparé en vue du clonage de différentes manières : il peut être excisé de l’ADN source à l’aide d’enzymes de restriction, amplifié par PCR (réaction en chaîne par polymérase) ou assemblé à partir d’oligonucléotides individuels. En parallèle, un vecteur plasmidique linéarisé est préparé par restriction enzymatique ou par PCR. Un plasmide est un petit fragment d’ADN circulaire répliqué au sein de l’hôte et indépendant du chromosome ou du génome de celui-ci. L’ADN d’intérêt est inséré dans le vecteur plasmidique via des liaisons phosphodiester pour former un nouveau plasmide recombinant qui sera répliqué par l’hôte.
Les vecteurs plasmidiques permettent à l’ADN d’intérêt d’être copié en grande quantité et fournissent souvent les éléments de contrôle nécessaires à la transcription et à la traduction de l’ADN cloné. Les plasmides constituent ainsi un outil polyvalent utilisé dans de nombreuses méthodes de biologie moléculaire, telles que l’expression de protéines, les études d’expression de gènes et l’analyse fonctionnelle de biomolécules.
Durant le processus de clonage, les extrémités de l’ADN d’intérêt et du vecteur doivent être modifiées de façon à les rendre compatibles en vue d’être reliées par une ADN ligase, une recombinase ou un mécanisme de réparation de l’ADN in vivo. Ces étapes font généralement appel à des enzymes telles que des nucléases, phosphatases, kinases et/ou ligases. De nombreuses méthodes et, plus récemment, des kits de clonage ont été développés afin de simplifier et de standardiser ces processus.
Biologie de synthèse
La biologie de synthèse est une branche émergente de la biotechnologie, dans laquelle les gènes et les protéines sont considérés comme des pièces détachées ou des dispositifs pouvant être remaniés et/ou assemblés de manière innovante, afin de créer une nouvelle fonctionnalité utile. Les avancées récentes en matière de production de biocarburants, de synthèse de produits biochimiques et de compréhension du génome minimal reposent sur des approches de biologie synthétique.
Ces projets ont souvent recours à l’assemblage de différentes séquences d’ADN pour créer de grandes structures artificielles, avec des méthodes optimisées de façon à simplifier le processus.
NEBuilder® HiFi DNA Assembly et Gibson Assembly® peuvent être utilisés pour construire diverses structures d’ADN, en allant d’une simple jonction de deux gènes métaboliques à la création d’un génome artificiel.
Plus d’informations disponibles dans la section Ressources Techniques ou sur neb.com